ПИШЕ: Милан Радуловић ([email protected])
Објављено: 24.8.2019. | Допуњено: 24.8.2019.
Опште напомене:
Хаплогрупа L настала је из предачке хаплоскупине LT, када је проистекла из ње прије 42.000 година, док је заједнички предак свих L грана живио прије 24.000 година на простору Таџикистана. Дијели се на L1 и L2 хаплогрупу. Хаплогрупа L1 грана се на три велике гране, L1a1-M27 која је карактеристечна за простор јужне и југоисточне Азије, L1a2-M357 карактеристичну за централну и западну Азију и L1b која има своја жаришта у Европи, Малој Азији и Леванту. L2 представља једну од најређих хаплогрупа на свијету. Среће се махом у Европи, а регистрована је још и у југоисточној Анадолији, Каквакзу, Русији (Татарстану). Хаплогрупа L може се повезати са Цивилизацијом долине Инда, Кура-Араксес и Мајкоп културом; Дравидима, Паштунима, Белуџима и другим јужно-азијским народима. Такође се може повезати и са Грцима Понта и Анадолије, посебно L1b линије.
Поријекло и миграције
Хаплогрупа L настала је прије 42.600 година, а живјела је на ивици изумирања до прије 24.100 година када је живио заједнички предак свих L линија (YFull, 2019). За мјесто поријекла сматра се Таџикистан, односно планински вијенац Памир, наводе Махал и Мацукас (Mahal & Matsoukas, 2017). Даље се грана на L1 и L2 хаплогрупу. Грана L1a развила се на подручју између западног Пакистана и Индије, док су L1b и L2 рано мигрирали у правцу западне Азије и Закавказја.
Неолит и енеолит
L1a-M2481 током неолита и енеолита
Хаплогрупа L1 грана се на двије гране L1a и L1b, које су формиране прије 18.000 година. Током неолита и енеолита гране L1a, M357 и M27 заступљене су на широком простору од западног Ирана и Закавказја до јужне Индије, са примарним жариштем у западном Пакистану и Индији. Са ширењем пољопривреде из правца централног Загорса, постају први пољопривредници јужне Азије. Представљајући основну хаплогрупу високо развјене Мергар културе (7.000-3.300. п.н.е.). Највећу разноврсност хаплотипова биљежи у Индији гдје је према Триведију и срардницима (Trivedi, Sahoo, Singh, Bindu, & Banerjee, 2007) разноврсност ±0.998. Што заједно са високом фреквенцијом иде у прилог старости хаплогрупе на подручју јужне Азије. Током енеолита проширили су се до Закавказја гдје је нађена L1a1-M27 у три узорка у Арени пећини у Јерменији, I1634 (4330-4060 п.н.е.), I1632 (4230-4000 п.н.е.), I1407 (4350-3500 п.н.е.), датованих у енеолит (Lazaridis, et al., 2016).
Са настанком Цивилизације долине Инда 3.300. п.н.е. становништво се из Мергара сели ка долини Инда заснивајући велике градове Мохенџо-даро, Харапа и Лотал. Гдје је L1a била претежна хаплогрупа, поред J2-M172.
L1b-M317 током неолита и енеолита
Хаплогрупа L1b коју дефинише снип M317 такође је као и L1a настала на простору западног Пакистана у долини Инда, гдје је и данас присутна са око 1,14% (Sengupta, et al., 2006). Но за разлику од L1a линија, среће се углавном у друштвеним скупинама које говоре индо-европске језике, закључујући према резултатима из поменутог рада и резултатима из студије Ди Кристофара (Di Cristofaro, et al., 2013). Заједнички предак свих L1b мушкараца живио је прије 12.700 година. Примарни центар хаплогрупе је на Леванту гдје је највећа заступљеност и разноликост, док је значајан дио популације данас присутан у Европи, што нас доводи до закључка да је L1b-M317 имала рано миграцијско раздвајање од L1a линија. Закључујући према данашњој распрострањености, учесталост и разноликости L1b хаплогрупе, развила се на подручју сјеверног Ирака.
Како за сада није нађена у древној ДНК првих фармера Леванта, те како изостаје из неолитских узорка Анадолије и како је имала прилично рано раздвајање од других L линија, намеће се питање временског оквира ширења популације. Претпостављајући са друге стране да је L1b-M317 била једна од линија Кура-Араксес (3.400-2.000 п.н.е.) културе (Hay, 2018) и узмајући у обзир да су братске L1a и L2 линије нађене у узорцима из енеолитског Закавказја (4.300 п.н.е.) и касног Мајкопа (3.400 п.н.е.), можемо закључити да су L1b мушкарци започели демографско ширење крајем енеолита на подручју између Закавказја и сјевера Ирака.
L2-L595 током неолита и енеолита
Представља једну од најређих хаплогрупа на свијету. За сада је пронађена код неколицине тестираних. Проистекла је из очинске L-M20 скупине прије 23.000 година, на подручју Таџикистана. Рано је мигрирала према Кавказу независно од L1 линија гдје се развијала и формирала примарно жариште. У старим костима пронађена је на локалитету Тепе Хисар на сјевероистоку Ирана, локалитету који представља касно енеолитско и рано бронзанодобско налазиште.
Бронзано и гвоздено доба
Током бронзаног доба долази до значајнијег демографског ширења L-M20 грана према централној и западној Азији. Значајан утицај на експанзију хаплогрупе L-M20 имале су следеће културе: Бактријско-Маргиански археолошки комплекс са подручја источног Туркменистана, јужног Узбекистана, сјеверног Афганистана и западног Таџикистана; Цивилизација долине Инда из Пакистана; те Кура Араксес и Мајкоп са простора Закавказја.
L1a-M2481 током бронзаног и гвозденог доба
Епицентар M2481 током бронзаног доба био је на простору Бактријско-Маргианског археолошког комплекса (БМАК) који се како смо већ раније поменули налазио на простору између источног Туркменистана, јужног Узбекистана, сјеверног Афганистана и западног Таџикистана. Поред данашње високе заступљености хаплогрупе на поменутом подручју и њене разноврсности (разноврсности хаплотипова). На жаришно присуство током бронзаног доба упућују и налази старих костију односно древне ДНК.
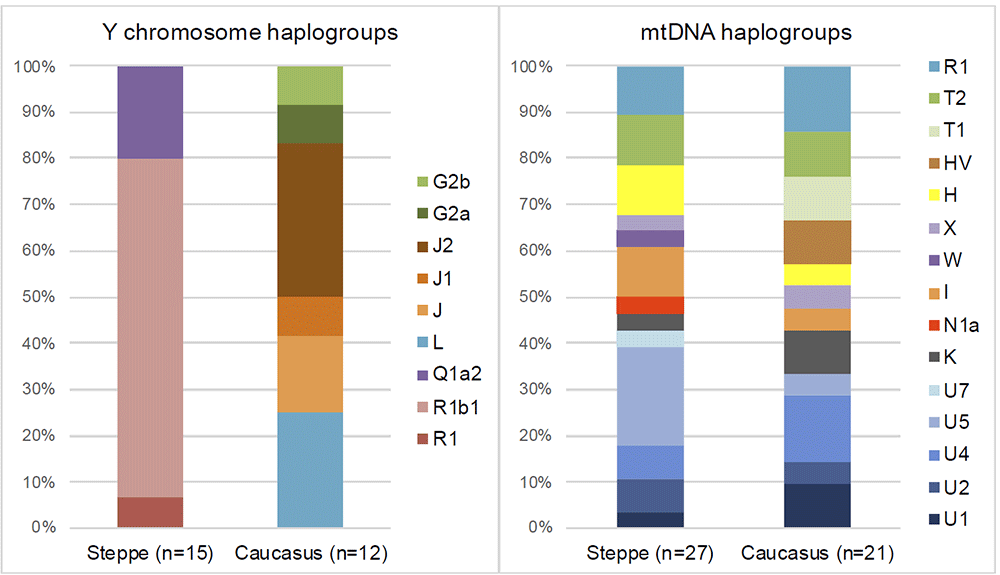
Према налазима из студије Нарасимхана и сарадника из 2018. године (Narasimhan, et al., 2018), у тестираној мушкој популацији БМАК, од 18 скелета, 2 су L1a хаплогрупе. Узорак I5604 датиран је у период 1880-1697 п.н.е., а I4285 у 1873-1661 п.н.е.. У популацији БМАК нађена су 4 узорка J2a, по два узорка E1b1, R2a, G и J хаплогрупе и по један R1b1, J1, R, T. Из студије се закључује да је евидентно кретање популације у смијеру запад-исток односно из правца Анадолије и Леванта ка истоку. Надаље, закључује се да је популација БМАК већински локалног енеолитског континуитета и да нема битнијег степског утицаја. Још се наводи, да групације које окружују БМАК немају степско поријекло до 2.100 п.н.е., те да се утицај степских популација евидентира тек у периоду имеђу 2.100-1.700 п.н.е..
Тако да налази које добијамо из „древне ДНК“ сугеришу да су носиоци L-M20 хаплогрупе започели ширење у централну Азију тек у периоду после 1.700. п.н.е., и да се нису налазили у корпусу степске популације енеолита.
Док су се кретања L1a-M2481 ка унутрашњости Индије дешавала током мезолита сматра Сахо (Sahoo, et al., 2006). Но како је L-M20 присутан и у индо-европским кастама до око 7%, један дио L1a свакако је стигао са индо-европским миграцијама.

Што се тиче Закавказја, осврћући се на енеолитске узорке из Јерменије, M2481>M27, те L2 из Мајкопа, врло је могуће да су L-M20 (M2481, L595) мушкарци били једни од носилаца мајкопске културе и да су се у каснијој сложеној интеракцији са Кура-Араксес културом ширили Анадолијом. Тако да су крајем бронзаног или почетком гвозедног доба прешли у Европу.
L1b-M317 током бронзаног и гвозденог доба
Када је ријеч о L1b линијама поред класичних метода, ослоњених на историју, заступљеност и разноврсност хаплогрупе, ми још увијек не располажемо налазима древне ДНК што у извјесној мјери отежава квалитетан приступ разумјевању миграционих односа. Стога смо при доношењу закључака поред осталог значајније ослоњени на општи однос и миграције хаплогрупа са којима су L1b-M317 у додиру.
Развила се прије 12 хиљада година на подрчју између Закавказја и Месопотамије, на шта упућује највећа разноврсност и заступљеност хаплотипова, о чему је било ријечи.
Током бронзаног доба учествовали су у популацији Кура-Араксес (3.400-2.000 п.н.е.) културе, која се протезала од источне Анадолије и Плодног полумјесеца на истоку до Ирана на западу. Припадници ове културе били су претежно J2a-L26, J1, G2a-L293, R1b, J2b, L1b, T1a-P77 Y-ДНК хаплогрупа (Радуловић и Новаковић, 2018).
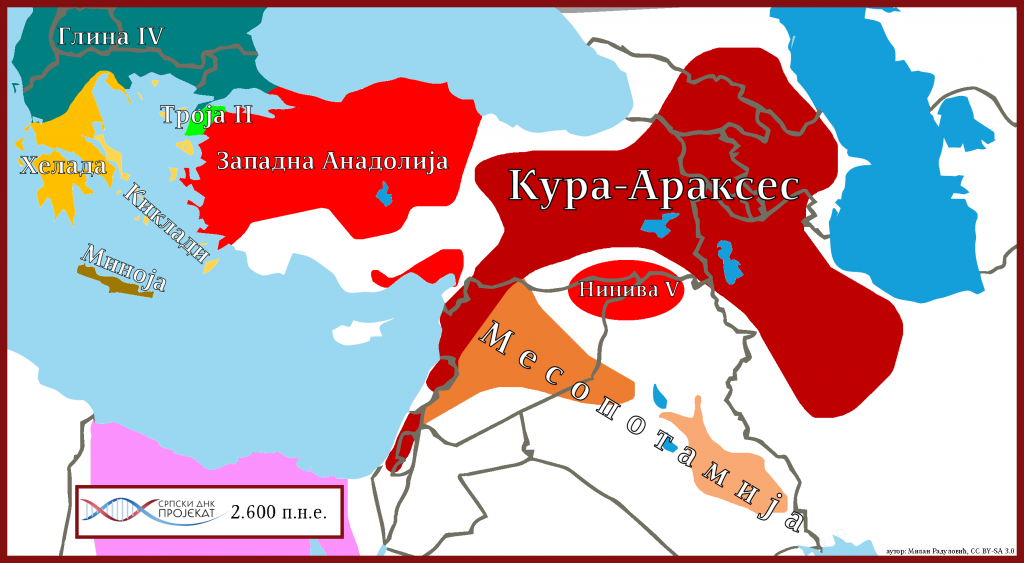
Како је Кура-Араксес идентификована као култура од посебног значаја за L1b хаплогрупу, сходно томе важно је напоменути да је ова култура била полу ратничког или релативно мирољубивог типа и као таква у литератури је означена. Она је имала утицаја на културе Анадолије, те на острво Кипар наводе Ализадех и сарадници (Alizadeh, Eghbal, & Samei, 2015), а још је могуће имала и утицаја на Крит преко Анадолије. Према бројним ауторима управо је Кура-Араксес утицала на колапс Урука (4.000-3.100 п.н.е.) (Kohl, 2007), што је могуће утицало на ширење L1b популације у правцу југоистока, али и Арабијског полуострва.
Тако да одговоре на миграционе процесе L1b популације ка Европи и медитеранском појасу треба тражити превасходно у експанзији Кура Араксес културе. Још је битно имати у виду да су на простору Кавказа, односно на простору Мајкоп културе пронађени припадници L1a и L2 хаплогрупа (Lazaridis, et al., 2016; Wang, et al., 2018; Рајевац, 2019), а знајући да је Кура Араксес географски у додиру са простором на коме се налазила Мајкоп култура (3.700-3.300 п.н.е.); сасвим је за претпоставити да су и L1b мушкарци били присутни у Мајкоп култури, а чији су представници претежно били J2a-L26, J1, L1a, G2, L2, J2b мушкарци.
L2-L595 током бронзаног и гвозденог доба
Кретање L595 током историје нешто је теже испратити услед малобројности скупине. Наиме, за сада је тестирано свега 15-ак људи који су припадници ове ријетке хаплогрупе. За потпору теза које ћемо изнијети ослонићемо се на налазе древне ДНК, односе хаплогрупа са којима су у додиру и на тренутну распрострањеност.
У раду Ванга и сарадника индентификовани су три узорка L хаплогрупе који се везују за касни Мајкоп, а за које Рајевац (Рајевац, 2019) прецизира да су L2. То су следећи узорци под шифрама: MK5004 процјењене старости између 3.347-3.095 п.н.е.; MK5001, 3.348-3.035 п.н.е.; и SIJ002.A0101, старости 3.349-3.033 п.н.е. Поред поменутог рада L2 је нађен још у раду (Narasimhan, et al., 2018) гдје је идентификован под шифром I2923, датиране старости између 2.878-2.636 п.н.е., на локалитету Тепе Хисар у источном Ирану.
Кавказка култура Мајкоп препозната је као култура са значајним удјелом L2 хаплогрупе, а као што смо раније навели, њени мушки представници претежно су били J2a-L26, J1, L1a, G2, L2, J2b темељећи на резултатима археогенетике и данашње присутности хаплогрупа на подручју Кавказа и околине.
Најближи заједнички предак L2 хаплогрупе
За потребе писања овог рада идентификовали смо 15 хаплотипова за које се основано сматра или је путем SNP теста потврђена припадност L2 хаплогрупи, а за које ћемо колективном квадратном методом, методом одступања од модала и уз помоћ NevGen Genealogy Tools v1.1 покушати утврдити вријеме најближег заједничког претка[1]. За једну генерацију просјечно смо узели 25 година колико се према Девин (Devine, 2005) препоручује при рачуници која броји више од 50 генерација до заједничког претка. Поред времена НЗП-а утврдићемо најспорије и најбрже маркере за ову хаплоскупину. Како би смо стекли одговарајуће оквире неопходне за даљу анализу.
Методологија
За прорачун узето је 13 L2 хаплотипова из јавне базе L хаплогрупе-ФТДНА (Y Haplogroup L Project, 2019) и то: N22419, 144196, N62831, N14510, 863058, 697332, 297364, 258180, 746307, 215799, 38049, 302190, N101576; те из базе Српског ДНК пројекта, 103625 као и један анонимни хаплотип са подручја Зете. Коришћена је колективна квадратна метода; метода одступања од модала; и рачунарски програм NevGen Genealogy Tools v1.1. За једну генерацију узет је просјек од 25 година. Средња вриједност STR за свих 15 хаплотипова на Y67 маркера je:
| DYS393 | DYS390 | DYS19 | DYS391 | DYS385 | DYS426 | DYS388 | DYS439 |
| 11 | 22 | 13 | 10 | 12-15 | 11 | 12 | 12 |
| DYS389i | DYS392 | DYS389ii | DYS458 | DYS459 | DYS455 | DYS454 | DYS447 |
| 12 | 16 | 28 | 12 | 9-9 | 11 | 11 | 25 |
| DYS437 | DYS448 | DYS449 | DYS464 | DYS460 | YGATAH4 | YCAII | DYS456 |
| 15 | 20 | 25 | 12-15-16-17 | 9 | 10 | 18-22 | 16 |
| DYS607 | DYS576 | DYS570 | CDY | DYS442 | DYS438 | DYS531 | DYS578 |
| 14 | 17 | 13 | 32-35 | 11 | 10 | 11 | 8 |
| DYF395S1 | DYS590 | DYS537 | DYS641 | DYS472 | DYF406S1 | DYS511 | DYS425 |
| 16-16 | 7 | 11 | 10 | 8 | 12 | 9 | 12 |
| DYS413 | DYS557 | DYS594 | DYS436 | DYS490 | DYS534 | DYS450 | DYS444 |
| 21-23 | 14 | 13 | 12 | 12 | 16 | 8 | 13 |
| DYS481 | DYS520 | DYS446 | DYS617 | DYS568 | DYS487 | DYS572 | DYS640 |
| 25 | 22 | 14 | 12 | 11 | 14 | 10 | 11 |
| DYS492 | DYS565 |
| 13 | 11 |
Квадратни метод, рачуница за НЗП
Овај метод рачунице је најзахвалнији за све врсте хаплотипова и њихову међусобну калкулацију (Klyosov & Kilin, 2016). Како ми у одабраној скупини имамо хаплотипове са различитим бројем маркера, ова метода рачунице била би и најадекватнија. Најближи заједнички предак за свих 15 особа према ККК111 живио је прије 3.408±582 година.
Одступање од модала, рачуница за НЗП
Како узетих 15 хаплотипова међусобно има различит број маркера, те стога имају и различит број међусобно упоредивих маркера, за потребе рачунице НЗП методом одступања од модала одредили смо стандард Y17 (Yfiler) као оптилмалан; односно који сви у већој или пуној мјери испуњавају. Средња вриједност Y-STR на Y17 маркера поређаних по ФТДНА редоследу je:
| DYS393 | DYS390 | DYS19 | DYS391 | DYS385 | DYS439 | DYS389i | DYS392 |
| 11 | 22 | 13 | 10 | 12-15 | 12 | 12 | 16 |
| DYS389ii | DYS458 | DYS437 | DYS448 | Y-GT4 | DYS456 | DYS438 | DYS635 |
| 28 | 12 | 15 | 20 | 10 | 16 | 10 | 21 |
Уочена су 74 одступања од модала. При стандардној стопи мутације по хаплотипу на стандарду Y17 (Yfiler) од 0,034 добијамо резултат 145 генерација до заједничког претка, односно ~3.627 година. Но када израчунамо λ= просјечан број мутација по маркеру кориговано за повратне мутације и подјелимо са константом брзине реакције од 0,002; добијамо резултат од 169 генерација до заједничког претка.
Односно ако узмемо да је једна генерација 25 година добијамо резултат од ±4.225 година до најближег заједничког претка.
NevGen Genealogy Tools v1.1, рачуница за НЗП
Према исходу рачунице на 95% вјероватноће, од заједничког претка прошло је 142 генерације, односно око 3.550 година.
Варијабилност маркера
Највећа варијабилност на стандарду Y17 биљежи се на маркерима: DYS391, DYS385b, DYS439; DYS389ii; DYS456. Односно најстабилнији маркери су DYS393, DYS390, Y-GATA-H4, DYS438
Исход
Дакле, прорачун времена НЗП-а за свих 15 хаплотипова креће се од 3.408 до 4.225 година. Односно предак L2 мушкараца живио је у периоду интезивног успона анадолских култура бронзаног доба.
Како L2 изостаје у данашњој популацији Мале Азије, Персије и Леванта, мала је вјероватноћа да су учествовали у популацији Кура-Араксес културе, па би миграционе токове L595 популације смјестили у шири контекст бронзанодопске Мале Азије.
Антика и средњи вијек
Гледајући у европским оквирима[2], хаплогрупа L-M20 среће се претежно у границама некадашњег Римског царства као и J2-M172, али с`тим да нема равномјернију присутности у границама римске државе као J2. Већ је данашња концентрација интезивна на некадашњој граници Римског царства, на коридору ријеке Рајне.
У Европи су махом присутни L1b хаплотипови, док је у Данској и сјеверним дијеловима Њемачке присутна и L1a, посебно M357 грана. У недавно објављеном раду о древним геномима из викиншког периода (Margaryan, et al., 2019), два од 300[3] анализираних мушких скелета припадали су L хаплогрупи. Узорак са шифром VK538 из Апулије датиран у средњи вијек, припадао је L1a-SK1426 хаплогрупи, док је узорак под шифром VK355 из Шеведске, Оланда, датиран у викиншко вријеме[4] припадао L2 хаплогрупи.
Осим медитеранских миграционих праваца L хаплогрупе према и унутар Европе, дио L-M20 могао је стићи и са кретањима аварских и хунских народа, посебно имајући у виду заступљеност L1b-SK1412 у Дагестану, те налаз древне ДНК хунског племића из Паноније, који је припадао L1a хаплогрупи.
SNP мутације
Хаплогрупу L дефинишу снипови M20, M11, M61, M185 и M295 (Karafet T. M., et al., 2008) ; она се дијели на три гране L1a, L1b и L2:
- L1a дефинишу следеће SNP мутације: M2481, M2565, M2605, M2664, Y5525/Z20163, Y5560/Z20168
- L1b дефинишу следеће SNP мутације: M317/ FGC36877, L655, PH982, PH1071, PH1379, PH2312, PH2342, PH3435, PH3443, PH3615, PH3912, PH4035, PH4159, PH4188, SK1413
L2 дефинишу следеће SNP мутације: L595, L877/PF5780, Page6/PF5751
Табела 1, основне гране и снип мутације
| Y-ДНК | ISOGG | SNP еквиваленти |
| L-M20 | L | M20/PF5570 * M11 * M2437 * M2666 * M2607/S7544 * PF5790 * M2391 * Z20190/Y5564 * M2528 * PF5815/M2598 * PF5821/M2613 * PF5792/M2569 * PF5705/M2390 * PF5725/M2430 * PF5791 * PF5754/M2485 * PF5787/M2556 * PF5692/M2362 * M2552 * Y5530/Z20173 * M185/PF5755 * M2490 * PF5841/M2670 * M2464 * Y5521 * M2386 * M2381 * PF5757 * PF5563/M2597 * PF5756/M2492 * PF5829/M2640 * M2358 * M2530 * M2680 * M2418 * Y5522/Z20156 * M2650 * M2479 * M2401 * PF5717/M2407 * PF5726/M2435 * M2673 * PF5743/M2463 * PF5683/M2356 * M61/PAGE43/PAGES00043 * PF5729/M2444 * PF5532 * M2676 * Y5517/Z20124 * PF5810/M2587 * PF5813/M2595 * M2628 * M2594 * M2612 * PF5775/M2536 * PF5785/M2554 * M2669 * L878/PF5524 * PF5750/M2482 * M2457 * PF5695/M2370 * PF5693/M2368 * L855 * M2621 * L656 * M2436 * PF5773/M2532 * PF5723/M2426 * M2365 * Y5529/Z20172 * PF5715/M2404 * PF5528/M2403 * PF5737/M2453 * M2474 * PF5783/M2551 * PF5710/M2395 * M2642 * M2583 * M2366 * M2564 * PF5539 * Y5540/Z20112 * PF5830 * Y23631 * L863 * M2383 * |
| L1-M22 | L1 | M2494 * M295 * M2496 * M22 * M2614 * M2593 * M2546 * M2639 * Y5524/Z20161 * M2635 * Z20155 * M2600 * M2617 * M2517 * Y6264/Z20194 * M2471 * M2631 * PAGE121/PAGES00121 * CTS2285/M2465 * M2384 * M2419 * Y5520/Z20128 * M2445 * M2416 * Y5528/SK1410/Z20169 * Y5537/Z20202 * Y5534/Z20201 * Y5533/Z20200 * M2665 * M2420 * Y5545/Z20129 * M2460 * M2394 * M2399 * Z20160 * M2586 * CTS6368 * M2405 |
| L1a-M2481 | L1a | Y5525/Z20163 * M2605 * M2498 * M2375 * SK1418/Y5565 * M2565 * M2481 * Z20195/Y5566 * Z20185/Y5563 * M2560 * M2462 * M2545 * M2664 * Y5560/Z20168 * M2555 * M2568 * Z20182/Y5562 * M2480 * Y15954 * M2357 * Z20135 * M2431 * M2623 * M2520 * Y5544/SK1417 |
| L1a-M27 | L1a1 | Z20393 * Z20452 * Z8046 * Z20570 * Z20415 * M27 * Z20413 * Z20442 * Z20436 * Z20385 * Z20450 * Z20360 * Y15614 * Z20382 * Z8049 * Z20397 * Z20361/SK1421 * Z20437 * Z20365 * Z20362/SK1419 * Z20356 * Z20367 * Z20354 * Z20443 * Z20379 * Z20380 * Z20416/SK1422 * Z20363 * Z8050 * M76 * Z20449 * Z20418 * Z20392 * Z20359 * Z20419 * Z20433 * Z20435 * Z20364 * Z20358 * Z20369 * Z20383 * Z20429 * Z20425 * Z20384 * Z20336 * Z20405 * Z20438 * Z20406 * Z20445 * Z20371 * Z20381 * Z20424 * Z20368 * Z20402 * Z20394 * L1321 * Z8048 * Y15772 * Z20388 * Z20370 * Z20440 * Z20444 * Z20337 * Z20401 * Z20410 * Z20411 * Y20687 * Z20357 * Z20412 * Z20441 * Z20428 * L1319 * Z20451 * Z20446/SK1420 * Y17739 * Z8044 * Z20345 * Y20688 * Z20434 * Z20414 * Z20427 * Z20417 * Z20398 * Z20400 * Z20399 * Z20422 * Z20404 * Z24638/Z24638.2 * Z20407 * SK1423/SK1423.2 * Z20390/F11470 * Z20386 * P329/P329.1/P329.2 * Z20448 * S24646 * Y17738 * L430 |
| L1a-M357 | L1a2 | M2461 * Y5531/Z20252 * M2523 * M2659 * Y5535/FGC32242 * M2574 * Y5518/SK1446 * M2469 * Y5536/FGC32244 * Y5556/Z20249 * FGC32245/BY945 * M2542 * M2429 * M2632 * M2402 * M2360 * M2618 * M2627 * Y5548/Z20240 * M2514 * Y5551/Z20243 * M2592 * M2364 * L1307 * M2558 * M2540 * M2475 * M2549 * M2535 * M2533 * Z20232 * Y5527/Z20248 * M2432 * M2476 * M2451 * Y5558/Z20250 * M2610 * M2355 * Z20254/Y5532 * Y5515/Z20229 * M2380 * M2634 * Z20210/Y5539 * Z20237 * Y32086 * Z20241 * Z20263/Y12414 * M2507 * M2561 * M2679 * Z20221 * M2630 * M2575 * Z20228 * M2662 * M2581 * M2393 * Y125839 * M2412 * M2459 * Z20233 * Z20230 * M2439 * M2606 * Y5567/Z20256 * M2681 * M2441 * Z20223 * M2458 * M2653 * M2608 * Y5550/Z20242 * M2371 * Y5554/Z20247 * M2387 * Y5552/Z20244 * M2557 * M357 * Y5557/FGC32246 * M2601 * Y5526/Z20246 * Z20227 * M2359 * Y5559/SK1447/Z20251 * M2424 * FGC40731 * Z20238 * Z20226 * M2524 * M2529 * Z20236 * FGC32241/Y6263 * M2672 * Y6298/Z20231 * M2515 * M2361 * M2367 * M2671 * M2590 * Y20049* |
| L1b-M317 | L1b | Y16218 * Y16217/FGC36810 * Y16215/FGC36805 * Y16196/FGC36796 * PH3443 * PH3615 * SK1413 * Y16198/FGC36793 * Y16372/FGC36795 * Y16365/FGC36802 * PH4188 * Y16377/FGC36781 * Y16383/FGC36822 * S7560 * PH4035 * PH1379 * Y16376/FGC36828 * PH3435 * Y16202/FGC36804 * Y16197/FGC36811 * PH2312 * PH1071 * Y16195/FGC36783 * PH4159 * Y16361 * PH982 * M317 * Y16367/FGC36794 * FGC36800 * Y19618/FGC49074 * Y16201/FGC36797 * PH1736 * Y16388/FGC36816 * Y16393/FGC36775 * Y16213/FGC36825 * Y16391/FGC36786 * PH2342 * PH3912 * FGC36776 * Y18412 * Y19619/BY12538 * Y11005 |
| L1b-M349 | L1b1 | FGC36778 * BY12542 * FGC36830 * FGC36812 * BY12543 * FGC36779 * FGC36788 * FGC36820 * FGC36829 * FGC36826 * FGC36821 * FGC36818 * FGC36787 * FGC36785 * M349 * FGC36777 * FGC36815 * FGC36782 * FGC36813 * FGC36827 * FGC36791 * FGC36790 * FGC36806 * FGC36817 * FGC36801 * FGC42525 * FGC42542 * FGC42546 * FGC42556 * FGC42555 * FGC42551 * FGC36780 * FGC36809 * FGC36824 * FGC36808 * FGC36823 * FGC36789 * FGC36799 * FGC36814 * FGC36819 * FGC42531 * CTS8901/S6469 * FGC320 * PAGE113/PAGES00113 * Y2357/S24423/FGC7623 * FGC42535 |
| L1b-SK1412 | L1b2 | Y16390 * Y134788 * Y16370 * Y16395 * Y16385 * SK1412 |
| L2-L595 | L2 | L595 * L877 / PF5780 * PF5769 * PF5838 * PF5758 * PF5762 * L870 * PF5691 * PF5808 * PF5740 / Z20586 * PF5682 * PF5742 * Z20579 * Page6/PF5751 |
Номенклатура
Табела 2, сачињена према: (Rosser, et al., 2000; Scozzari, et al., 2001; The Y Chromosome Consortium, 2002; Karafet T. , et al., 2008; ISOGG, 2019).
| L-SNP | Rosser et al. 2000 | Scozzari et al. 2001 | (α) | (β) | (γ) | (δ) | (ε) |
| L-M20 | 26 | 26.1/26.2 | 28 | VIII | 1U | 27 | Eu17 |
| L-M22 | 26 | 26.1/26.2 | 28 | VIII | 1U | 27 | Eu18 |
| L-M27 | 26 | 26.1/26.2 | 28 | VIII | 1U | 27 | Eu17 |
| L-M317 | |||||||
| L-M357 | |||||||
| L-L595 | |||||||
| (ζ) | (η) | YCC 2002 (Longhand) | YCC 2008 (Longhand) | ISOGG 2006 | ISOGG 2011 | ISOGG 2015 | |
| H5 | F | L* | L | L | L | L | |
| H6 | F | L* | L | L | L1 | L1 | |
| H5 | F | L1 | L1 | L1 | L1a | L1a1 | |
| L2 | L2 | L1b | L1b | ||||
| L3 | L3 | L1c | L1a2 | ||||
| L2 | – |
скраћенице из номенклатуре:
α-Jobling and Tyler-Smith 2000 and Kaladjieva 2001; β-Underhill 2000;
γ-Hammer 2001; δ-Karafet 2001; ε-Semino 2000; ζ-Su 1999;
YCC-Y Chromosome Consortium;
ISOGG-International Society of Genetic Genealogy.
Мапе распрострањености
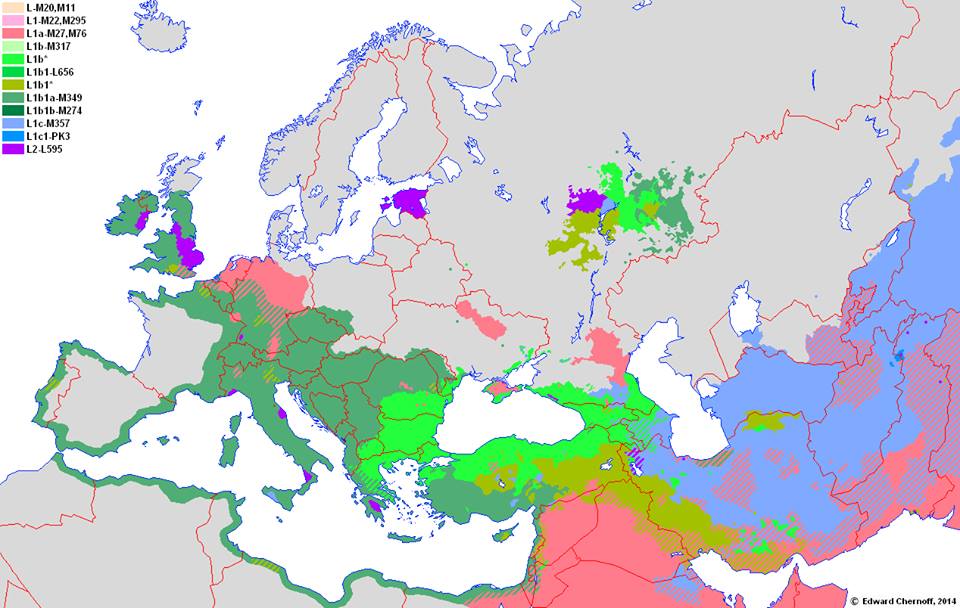
Стабло
Подгрупе и заступљеност
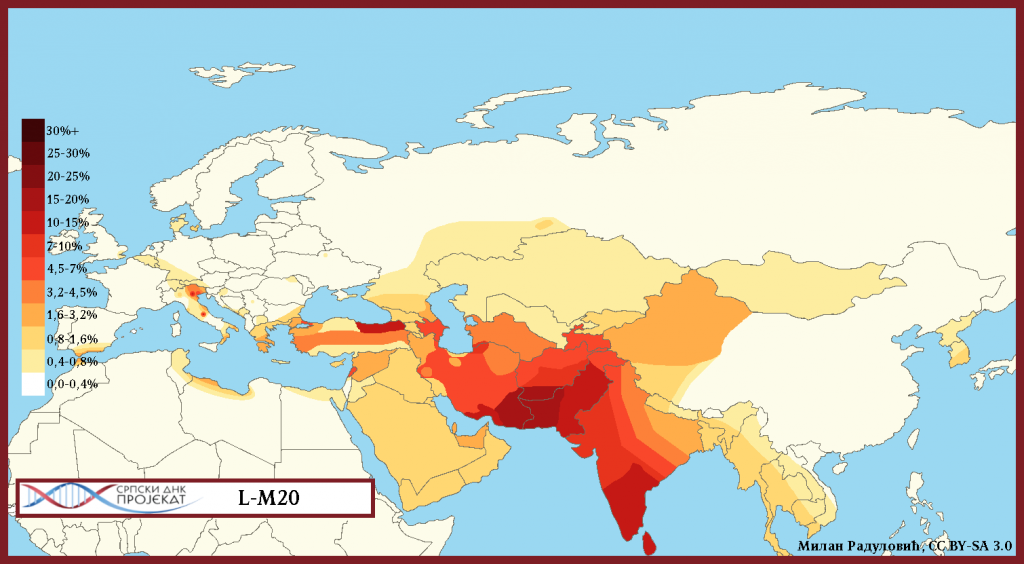
Хаплогрупа L-M20 најзаступљенија је у јужној Азији, у Индији, Пакистану, Авганистану. У Европи је највећа концентрација у сјеверној Италији, гдје је према студији из 2009. (Battaglia, et al., 2009) заступљена са 4,5%. Процентуално гледано најзаступљенија је у земљама: Шри Ланка 15%, Пакистан 13%, Авганистан 6,94%, Индија 6,73%, Иран 5%, Турска 4,2%.
| Процјена L-M20 популације у наведеним земљама | |||
| земља/народ/групација | узорак | проценат | ±популација |
| ЕВРОПА | 933 | 0,1% (Дибирова, 2011) | 376.919 |
| Аустрија-Тирол | 270 | 0,74% (Erhart, et al., 2012) | 2.761 |
| Белгија-Антверпен, Источна Фландрија | 540 | 0,74% (2012; Decorte, et al., 2012) | 6.456 |
| Бугарска | 808 | 0,2% (Karachanak, et al., 2013) | 6.845 |
| Грчка | 257 | 2,33% (Greek DNA Project , 2019) | 121.394 |
| Естонија | 74 | 1,35% (Scozzari, et al., 2001) | 8.384 |
| Италија | 817 | 0,24% (Grugni, et al., 2018) | 70.626 |
| Кипар | 344 | 1,2% (Heraclides, et al., 2017) | 5.058 |
| Мађарска | 535 | 0,37% (Hungarian_Magyar_Y-DNA_Project, 2019) | 17.284 |
| С. Македоници | 428 | 0,46% (Noveski, Trivodalieva, Efremov, & D., 2010; Jankova, Geppert, Videtic Paska, Willuweit, & Roewer, 2019; Macedonian DNA, 2019; Српски ДНК пројекат, 2019) (Battaglia, et al., 2009) | 4.600 |
| Срби | 2.997 | 0,13% (Српски ДНК пројекат, 2019) | 7.085 |
| Холандија | 85 | 1,17% (Karafet, et al., 2016) | 99.766 |
| Хрватска | 1.100 | 0,27% (Mršić, et al., 2012) | 5.351 |
| Шпанија-Андалузија | 29 | 3,4% (Semino, et al., 2000) | 142.598 |
| ЕВРОПА УКУПНО | 0,13%, минимална процјена | 498.208 | |
| АЗИЈА | |||
| Авганистан | 433 | 6,94%[5] (Di Cristofaro, et al., 2013) | 1.094.873 |
| Азербејџан | 72 | 6,9% | 325.024 |
| Грузија | 66 | 1,5% (Battaglia, et al., 2009) | 32.280 |
| Индија | 728 | 6,73% (Sengupta, et al., 2006) | 42.343.511 |
| Ирак | 203 | 0,99% (Abu-Amero, et al., 2009) | 166.830 |
| Иран | 5% (Grugni, et al., 2012) | 1.890.300 | |
| Јерменија | 413 | 1,93% (Herrera, et al., 2012) | 30.002 |
| Катар | 72 | 2,78% (Abu-Amero, et al., 2009) | 26.952 |
| Кореја | 506 | 0,59% (Kim, Han, Kim, & Kim, 2010) | 215.769 |
| Кина-Синкјанг | 546 | 2% (Hou, 2019) | 218.133 |
| Киргистан | 132 | 1,5% (Di Cristofaro, et al., 2013) | 40.860 |
| Либан | 916 | 5,24% (Abu-Amero, et al., 2009) | 112.450 |
| Малезија-Индијци | 301 | 17,27% (Chang, et al., 2008) | 173.788 |
| Монголија | 933[6] | 0,5% (Дибирова, 2011) | 7.606 |
| Пакистан | 176 | 13% (Sengupta, et al., 2006) | 13.505.349 |
| Палестина | 367 | 0,7% (Zalloua, et al., 2008) | 15.926 |
| Саудијска Арабија | 157 | 1,91% (Abu-Amero, et al., 2009) | 315.150 |
| Сирија | 202 | 5,4% (Zalloua, et al., 2008) | 460.751 |
| Таџикистан | 142[7] | 6,33% | 282.666 |
| Турска | 523 | 4,2% (Cinnioğlu, et al., 2004) | 1.722.081 |
| Узбекистан | 170 | 0,56% (Völgyi, et al., 2014) | 93.111 |
| УАЕ | 164 | 3,06% (Abu-Amero, et al., 2009) | 140.846 |
| Шри Ланка | 60 | 15% (Karafet, et al., 2016) | 1.625.250 |
| АФРИКА | |||
| Египат | 117 | 0,85% (Karafet, et al., 2016) | 412.424 |
| Либија | 173 | 1,73% (Immel, 2008) | 62.280 |
| Тунис | 220 | 0,45% (Fadhlaoui-Zid, et al., 2014) | 24.710 |
| УКУПНО | 65.837.130 | ||
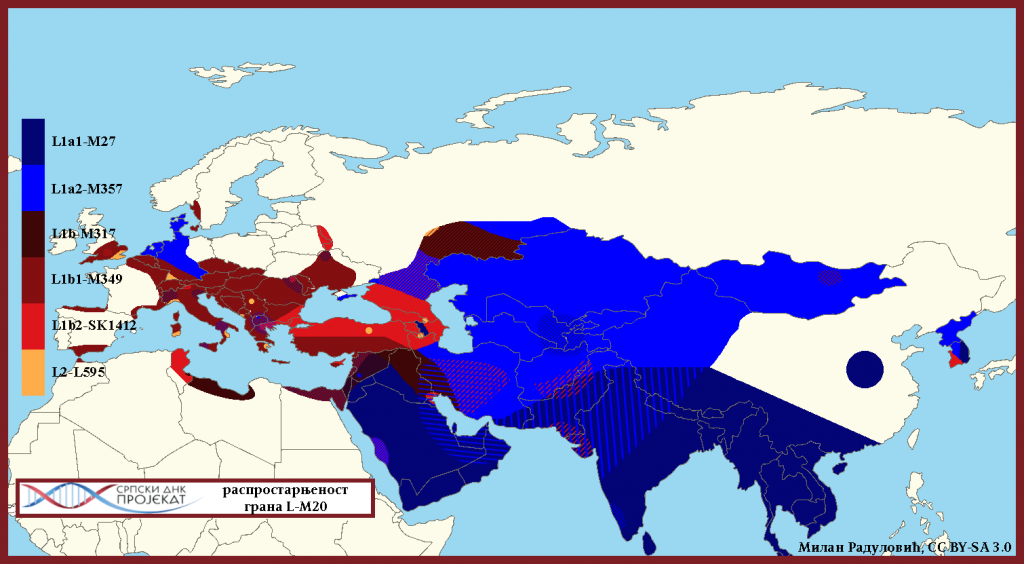
Следеће гране гравитирају:
L-M20>L595>
- Врло ријетка хаплогрупа. За сада је нађена код свега неколико десетина тестираних, и то у: Сардинији, Србији, Грчкој, Италији, Турској, Њемачкој, Русији, Енглеској, Ирској и Азербејџану.
L-M20>M22>M2481>М27>
- Ова грана L1a хаплогрупе најприсутнија је у јужној Азији, Индији и Пакистану; а препознатљива је и у Арабијском полуострву. Биљежи се и у Кини и на Леванту; а има и своје европске гране које се налазе претежно у медитеранском појасу. Грана се на двије гране, Z20387 и Y31961 (доминантна грана Y31214).
- Z20387 карактеристична је за арабијско полуострво и јужну Азију. Даље се грана на двије велике гране: BY12397 коју за сада налазимо на Арабијском полуострву и L1320 која је претежно јужноазијског карактера, но која има и своје арабијске и левантске гране.
- Y31961 дијели се на Y31961* и Y31213. Грана Y31213 заступљена је од Леванта преко Арабије до централне Азије.
L-M20>M22>M2481>M2533>M357>
- Препознатљива је централноазијска грана L1a хаплогрупе. Ова грана има јако старе гране и у Арабији и Леванту. Грана се на четири гране: M2398 (M2398>Y12415 гравитира Таџикистану), Y6288, Y44848 (Арабијско полуострво) и BY198125.
L-M20>M22>M2481>M2533>M357>Y6288>Y6259>Y6284>Y6266
- Y6266 је грана која је карактеристична за Чечене, код којих је L1a-M357 заступљена са 7,2%. Старост гране је ±3.300 година.
L-M20>M22>M317>
- L1b је грана која има своје матично подручје на простору Закавказја и сјевера Ирака, одакле се током бронзаног доба проширила у Европу. До заједничког претка броји око 12.500 година. Грана се на двије гране SK1412 и M349.
L-M20>M22>M317> SK1412
- Гравитира Понту и Анадолији, што је и базна територија хаплорупе, заједно са Закавказјем; простор на коме се хаплоскупина и развила. Присутна је од Европе и Медитерана до централне и источне Азије. Грана се на двије велике гране FGC51074 и Y16366.
- FGC51074 раширена је од источног Медитерана до Британије. Са Левантом као матичним подрујем.
- Y16366 је понтско-кавкаска грана, које се дијели на Y16187 и Y16366*.
L-M20>M22>M317> SK1412> Y16366
- Понтско-кавкаска грана дијели се на Y16187 и Y16366*:
- Y16187 је једна од препознатљивих хаплогрупа Грка са Понта и из Анадолије, гдје је L1b-M317 присутна са око 17% од укупне мушке популације. Низводна Y18413>Y18891 поред Понта присутна је у Грузији и међу Аварима.
- Y16366* идентификована је на широком подручју између источне Анадолије и Кавказа.
L-M20>M22>M317>M349
- Раширена је на простору Европе идуж Медитерана. Среће се и у кавкаском региону. За сада су идентификоване три низводне гране: B374, FGC36845 и Y31183.
- B374 назван још и Рајна-Дунав-Волга кластер, по матичном подручју хаплоскупине, кластер је иксључиво европски.
- FGC36845 раширен је диљем Европе, Медитерана, а среће се и на Леванту.
- Y31183 махом се среће на Леванту, али је такође као и сви огранци M349 присутна на подручју Европе.
- Код нас је водећа хаплогрупа од L-M20, чије се матично подручје на простору српске земље налази на потезу Требиње-Бјелопавлићи-Грбаљ.
Стари народи
L-M20 може се повезати са старим народима Анадолије и њиховим државама, Хетитима и Лидијцима; са левантским народима Феничанима и Филестејцима; Персијанцима; Дравидима и другим са подручја јужне Азије; али и са Хунима и Аварима.
Филестејци
Закључујући према резултатима студије „Ancient DNA sheds light on the genetic origins of early Iron Age Philistines“ и налзу ASH087.A0101[8] који је L хаплогрупе, утврђено је да су учествовали у етногенези Филестејаца (Feldman, et al., 2019). Према резултату из поменутог рада, утврђено је да поменути Филестејац и његов кластер ASH_IA2 немају европске примјесе за разлику од групе ASH_IA1 код којих је она око 14%, што указује на локално левантско поријекло и оно становништво које се инкорпорирало у филестејску популацију[9].
Феничани
Сасвим је извјесно да су учествовали у етногенези Феничана на шта упућује претходно поменути рад који свједочи о присуству популације на Леванту, али и појачано присуство у регијама у којима су Феничани били активни, као што су Андалузија, сјевер Африке, југ Италије.
Хетити и други анадолски народи
Према данашњој и недавној (прије 1922.г.) демографској слици; односно распрострањености, учесталости (4-12%) и разноврсности L1 хаплоскупине на подручју источне и сјевероисточне Анадолије; сасвим је извјесно да су и L-M20 мушкарци имали удјела у древним цивилизацијама Анадолије. Посебно указавши на бројне археогенетске налазе са подручја кавкаског региона из кога су текли правци миграција ка Анадолији.
Персијанци
Несумњиво је потврђена аутохтоност хаплоскупине на подручју Ирана гдје су археогенетски резултати додатно потврдили старост скупине. У Ирану су равномјерно распоређени на цијелој територији што указује на рано учешће у етногенетским процесима.
Хуни
Како је у свом раду Дибирова навела, заступљеност хаплогрупе на простору Евроазијске степе је 0,5% (Дибирова, 2011) што је мало, али је археогенетским налазом из Мађарске бр. 12763 (Джансугурова, и др., 2017) халогрупа L потврђена код Хуна. Нађена је у поменутом узорку који је припадао хунском племићу. Узорак датиран у ±500. годину. Резултатом је утврђена заступљеност хаплогрупе код Хуна, али је остала загонетка у ком омјеру је учествовала у хунској популацији. Из узорка су извучени следећи STR маркери, разврстали смо их по ФТДНА редоследу:
| DYS393 | DYS19 | DYS385 | DYS439 | DYS389i | DYS389ii |
| 16 | 14 | 7-8 | 19 | 10 | 24 |
| DYS458 | DYS437 | YGATAH4 | DYS456 | DYS438 | DYS635 |
| 14 | 16 | 7 | 15 | 12 | 20 |
На основу хаплотипа можемо закључити да се ради о L-M20>M22. Ближу грану са већом сигурношћу не можемо идентификовати, али се на основу маркера уочава оквирна сличност са M357 хаплотиповима. Прије свега ниске вриједности DYS385 маркера које се срећу искључиво код M357. Већина предвиђача Y-ДНК хаплогрупе не може препознати хаплогрупу на основу хаплотипа, док „World Haplogroup & Haplo-‘I’ Subclade Predictor“, за хапловрсту предвиђа L3 односно M357.
Српске земље
У српским земљама идентификоване су следеће хаплогрупе: L1b-M349>BY12542, L2-L595 које су махом стациониране у Црној Гори/Приморју; и L1a-M357 која гравитира Повардарју.
L1b-M349>BY12542, Доброгорани
Најбројнији је кластер L хаплоскупине у српској земљи, често га још називамо и Лазаревићи, по братству из чијег су се окружења разивла сва друга братства. Матична област рода је Приморје. Према анализи Вукићевића, стручњака за генетичку генеалогију Црне Горе, развој и миграције BY12542 братстава ишли су (Вукићевић, 2019):
- Лазаревићи су братство из Грбља које потиче из Шобајића у Бјелопавлићима. Од њих су Вујићи и Пејурићи у Бјелопавлићима;
- Од исељеника из Шобајића су братства: Вучуровићи, Водовари и Илићи у Кривошијама и Вукаловићи и Вучинићи у Доловима у Грахову која су мигрирала преко Загарача и Добре Горе у Цуцама, а по којој су прозвани Доброгоранима.
- У Загарачу су остали Радмановићи, разграната група братстава, који се рођакају са Доброгоранима, а ова веза је и генетски потврђена.
- Дио исељеника из Шобајића зауставио се на Кривошијама и од њих потичу Вукаловићи и Вујичићи у Зубцима и Грахову и Милошевићи у области Гацка и Невесиња.
- Од исељеника из Шобајића су братства: Вучуровићи, Водовари и Илићи у Кривошијама и Вукаловићи и Вучинићи у Доловима у Грахову која су мигрирала преко Загарача и Добре Горе у Цуцама, а по којој су прозвани Доброгоранима.
Према Вукићевићу (Вукићевић, 2019Б): „на основу предања о сродству и пореклу појединих братстава из Шобајића у Бјелопавлићима основано се може претпоставити да је присутна и у Бјелопавлићима, Грбљу, Љуботињу, Пиперима, Цеклину и Цуцама.“
Једна од карактеристика рода је и крсна слава Св. Петка коју слави већина рода, њих око 80%. У иностраним и научним базама података немају ни ближа ни далека поклапања.
Најближи заједнички предак
За потребе писања овог рада идентификовали смо хаплотипове из базе Српског ДНК пројекта на дан 29. јули 2019. године, за које се основано сматра или је путем SNP теста потврђена припадност BY12542 хаплогрупи. За које ћемо колективном квадратном методом, методом одступања од модала и уз помоћ NevGen Genealogy Tools v1.1 покушати утврдити вријеме најближег заједничког претка. Генерацију просјечно рачунамо 30 година.
Метдологија
Коришћена је колективна квадратна метода; метода одступања од модала; и рачунарски програм NevGen Genealogy Tools v1.1. За једну генерацију узет је просјек од 30 година. Средња вриједност STR за све идентификоване хаплотипова на Y23 маркера je:
| DYS393 | DYS390 | DYS19 | DYS391 | DYS385a | DYS385b | DYS439 | DYS389i |
| 13 | 23 | 14 | 10 | 15 | 19 | 12 | 13 |
| DYS392 | DYS389ii | DYS458 | DYS437 | DYS448 | Y-GH4 | DYS456 | DYS576 |
| 14 | 28 | 16 | 16 | 19 | 10 | 15 | 19 |
| DYS570 | DYS438 | DYS481 | DYS549 | DYS533 | DYS635 | DYS643 |
| 15 | 10 | 24 | 13 | 13 | 23 | 11 |
Квадратни метод, рачуница за НЗП
Овај метод како смо раније навели је најзахвалнији за све врсте хаплотипова и њихову међусобну рачуницу (Klyosov & Kilin, 2016). Како ми у одабраној скупини имамо хаплотипове са различитим бројем маркера, ова метода рачунице била би и најадекватнија. Најближи заједнички предак за све особе према ККК111 живио је прије 427±158 година.
Одступање од модала, рачуница за НЗП
Узети хаплотипови испуњавају Yfiler стандард, стога смо за потребе рачунице НЗП методом одступања од модала одредили Y17 (Yfiler) као оптилмалан, односно који сви у пуној мјери испуњавају.
Уочена су 22 одступања од модала. При стандардној стопи мутације по хаплотипу на при стандарду Y17 (Yfiler) од 0,034 добијамо резултат 40 генерација до заједничког претка, односно ~1.200 година. Када израчунамо λ= просјечан број мутација по маркеру кориговано за повратне мутације и подјелимо са константом брзине реакције од 0,002; добијамо резултат од 41,5 генерација до заједничког претка.
Односно ако узмемо да је једна генерација 30 година добијамо резултат од ±1.245 година до најближег заједничког претка.
NevGen Genealogy Tools v1.1, рачуница за НЗП
Према исходу рачунице на 95% вјероватноће од заједничког претка прошло је 42 генерације, односно око 1.200 година.
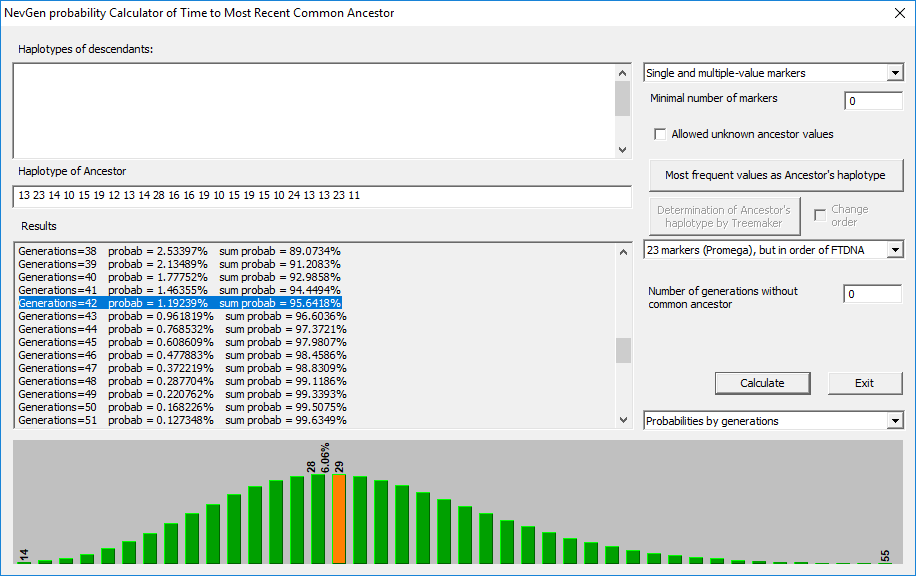
Исход
Прорачун времена НЗП-а за све узете хаплотипова креће се од 430 до 1.200 година зависно од рачунача. Двије од три рачунице поклапају се у исходу, односно према њима најближи заједнички предак живо је прије 1.200 година. Дакле негдје у 9. вијеку. Услед малог броја маркера и релативне малојбојности групе, треба бити обазрив при узимању резултата.
Разматрање
Доброгорани се могу посматрати кроз контекст братстава поријеклом из Шобајића у Бјелопавлићима, а која имају блиске, наизглед матичне везе са братством Лазаревића из Грбља.
У погледу прапоријекла за сада не можемо дати конкретне одговоре. Прије свега јер немамо идентификовану/тестирану низводну грану од BY12542 из које проистиче род, надаље немамо репрезентативан број тестираних са већим бројем маркера што би нам омогућило квалитетнију НЗП рачуницу. Род нема поклапања са другим L1b хаплотиповима и нема блиских кластера уназад хиљадама година, што додатно отежава реконструкцију миграције ка Балкану. Индиције иду у правцу источног поријекла групе, а заједно са старошћу од 1.200 година смијешта га у грко-ромејски супстрат српског етноса.
Стара ДНК
До сада је најстарији пронађени узорак L хаплоскупине датиран у енеолит 4.350-3.500 п.н.е., I1407, нађен у Арени пећине на простора Јерменије. Археогенетски налази махом су нађени на простору кавкаског региона и Бактријско-Маргианског археолошког комплекса. У табели која слиједи, наведени су сви досадашњи налази L хаплоскупине:
Табела 3, древна L
| шифра | датовање | простор | држава | Y-ДНК | мт-ДНК | студија |
| I1634 | 4.330-4.060 п.н.е. | Арени пећина | Јерменија | L1a1-M27 | H2a1 | (Lazaridis, et al., 2016) |
| I1632 | 4.230-4.000 п.н.е. | Арени пећина | Јерменија | L1a1-M27 | K1a8 | – |
| I1407 | 4.350-3.500 п.н.е. | Арени пећина | Јерменија | L1a1-M27 | H | – |
| DA85 | 169-250 н.е. | Курган бр. 2, Жапарик | Киргизија | L1a1-M27>Y31961* | (Damgaard, et al., 2018) | |
| I5604 | 1880-1697 п.н.е. | Бустан | Узбекистан | L1a | K1a1 | (Narasimhan, et al., 2018) |
| I4285 | 1873-1661 п.н.е | Сапали Тепе | Узбекистан | L1a | U7a3 | – |
| S10001.E1.L1 | 1300-1000 п.н.е. | Лое Банр 1 | Пакистан | L1a | R30b1 | – |
| I8220 | 970-550 п.н.е. | Алиграма | Пакистан | L1a | .. | – |
| I6555 | 906-820 п.н.е. | Лое Банр 1 | Пакистан | L1a | M4 | – |
| S10974.Y1.E1.L1 | 900-800 п.н.е. | Лое Банр 1 | Пакистан | L1a | .. | – |
| I6554 | 831-796 п.н.е. | Лое Банр 1 | Пакистан | L1a | T2g1 | – |
| S7721.E1.L1 | 500-300 п.н.е. | Сват долина, Сајду Шариф | Пакистан | L1a | R6b | – |
| I2923 | 2878-2636 п.н.е. | Тепе Хисар | Иран | L2 | W3b | – |
| MK5004 | 3347-3095 п.н.е. | Маринскаја 5 | Русија | L2 | T2al | (Wang, et al., 2018) |
| MK5001 | 3348-3035 п.н.е. | Маринскаја 5 | Русија | L2 | K1a4 | – |
| SIJ002.A0101 | 3349-3033 п.н.е. | Синјуха | Русија | L2 | U4c1 | – |
| VK355 | 847 ± 65 н.е. | Оланд | Шведска | L2 | U5b1b1a | (Margaryan, et al., 2019) |
| VK538 | 11-13. вијек | Фођа | Италија | L1a1b-SK1426 | H+16291 | – |
| 12763 | 500 н.е. | Панонска низија | Мађарска | L1a2-M357 | D4j12 | (Джансугурова, и др., 2017) |
Познате личности
Сеид Аџал Шемсудин
Сеид Аџал Шемсудин ( 1211 , Бухара – 1279 ) први је гувернер царске династије Јуан у провинцији Јунан. Учесник је монголских освајања у Бурми, а познат је по томе што је предак многим муслиманима широм Кине. Хаплогрупа L1a1-M27 (Wang, et al., 2013)

Ченг Хе (трад. кин. 鄭和, кин. 郑和; 1371—1435) био је кинески адмирал, поморац и истраживач. Истраживао је подручја југоисточне азије, Суматре, Јаве, Шри Ланке, Индије, Персије, Персијског залива, југозападне Азије, Црвеног мора, и Мозамбика. Надимак му је Сан Бао, па се спекулише о томе да се по њему назвао Синдбад. Потомак је чувеног Аџал Шемсудина. Хаплогрупа L1a1-M27.

Лука Вукаловић (Зупци, Требиње, 18. октобар 1823 — Салтакча, Одеса, Русија 6. јул 1873) је вођа српског устанка у Херцеговини 1852—1862. Књаз Данило именовао је Луку за војводу Зубаца, Крушевице и Драчевице. Хаплогрупа L1b-M349>BY12542.

Трипко Вукаловић (Зубци, Требиње, 1835 -Никшић, 1. април 1898) је један од устаничких вођа током Невесињске пушке, војвода је од Зубаца и најмлађи брат војводе Луке Вукаловић. Хаплогрупа L1b-M349>BY12542 род Доброгорана.
Литература:
Вукићевић, И. (2019, јун 20). Родови старобалканског порекла у Црној Гори: допуњено 20.6.2019. Преузето са Порекло: https://www.poreklo.rs/2017/11/19/rodovi-starobalkanskog-porekla-u-crnoj-gori/
Вукићевић, И. (2019Б, јул 14). Генетска слика Црне Горе: допуњено 14.7.2019. Преузето са Порекло: https://www.poreklo.rs/2017/11/19/genetska-slika-crne-gore/
Джансугурова, Л. Б., Джантаева, К. Б., Нуржибек, Жунусова, Г. С., Кузовлева, Е. Б., Мусралина, Л. З., . . . Хусаинова, Э. М. (2017). Выделение и анализ древней ДНК из костных человеческих останков гуннского периода. Серия биологическая и медицинская, 4(322), 39-50.
Дибирова, Х. Д. (2011). Роль географической подразделенности и лингвистического родства в формировании генетического разнообразия населения Кавказа (по данным об Y хромосоме). Москва: Учреждении Российской академии медицинских наук Медико-генетическом научном центре РАМН .
Радуловић, М., & Новаковић, Н. (2018). Хаплогрупа Ј2 (са освртом на српске земље). Београд: Друштво српских родословаца Порекло.
Рајевац, М. (2019). Хаплогрупа L-древна ДНК. Београд: Друштво српских родословаца “Порекло”: Српски ДНК пројекат.
Српски ДНК пројекат. (2019, Јул 23). Српски ДНК пројекат. Преузето са Порекло: https://dnk.poreklo.rs/DNK-projekat
Abu-Amero, K. K., Hellani, A., González, A. M., Larruga, J. M., Cabrera, V. M., & Underhill, P. A. (2009). Saudi Arabian Y-Chromosome diversity and its relationship with nearby regions. BMC Genetics, 1-9. doi:10.1186/1471-2156-10-59
Alizadeh, K., Eghbal, H., & Samei, S. (2015). Approaches to social complexity in Kura-Araxes culture: A view from Köhne Shahar (Ravaz) in Chaldran, Iranian Azerbaijan. Paléorient, 41(1), 37-54.
Battaglia, V., Fornarino, S., Al-Zahery, N., Olivieri, A., Pala, M., Myres, N. M., & Semino, O. (2009). Y-chromosomal evidence of the cultural diffusion of agriculture in southeast Europe. European Journal of Human Genetics, 820-830. doi:10.1038/ejhg.2008.249
Chang, Y. M., Jaya, P., Revathi, P., Phoon, Y., Jaya, P., & Jeevan, N. (2008, July 3). Population Malaysia [Indian]. Retrieved from YHRD: https://yhrd.org/YP000242-Malaysia+%5BIndian%5D
Cinnioğlu, C., King, R., Kivisild, T., Kalfoglu, E., Atasoy, S., Cavalleri, G., . . . Underhill, P. (2004). Excavating Y-chromosome haplotype strata in Anatolia. Human Genetics, 127-148. doi:10.1007/s00439-003-1031-4
Damgaard, P. d., Marchi, N., Rasmussen, S., Peyrot, M., Renaud, G., Korneliussen, T., . . . Pedersen, M. W. (2018). 137 ancient human genomes from across the Eurasian steppes. Nature, 557(7705), 369–374 . doi: 10.1038/s41586-018-0094-2
Decorte, R., & al., e. (2012, February 10). Population Oost-Vlaanderen, Belgium [Belgian]. Retrieved from YHRD: https://yhrd.org/YP000784-Oost-Vlaanderen%2C+Belgium+%5BBelgian%5D
Decorte, R., Larmuseau, M., & Ottoni, C. (2012, February 10). Population Antwerpen, Belgium [Dutch]. Retrieved from YHRD: https://yhrd.org/YP000781-Antwerpen%2C+Belgium+%5BDutch%5D
Devine, D. (2005, September/October). How Long Is a Generation? Ancestry Magazine, 23(5), 51-55. Retrieved from Ancestry: https://books.google.ba/books?id=JzgEAAAAMBAJ&lpg=PA1&hl=sr&pg=PA51#v=onepage&q&f=false
Di Cristofaro, J., Pennarun, E., Mazières, S., Myres, N. M., Lin, A. A., Temori, S. A., & Chiaroni, J. (2013). Afghan Hindu Kush: where Eurasian sub-continent gene flows converge. PloS one, 8(10), 1-12. doi:10.1371/journal.pone.0076748
Erhart, D., Berger, B., Niederstätter, H., Gassner, C., Schennach, H., & Parson, W. (2012, August 17 ). Frequency data for 17 Y-chromosomal STRs and 19 Y-chromosomal SNPs in the Tyrolean district of Reutte, Austria. International Journal of Legal Medicine, 126(6), 977–978. doi:doi.org/10.1007/s00414-012-0751-1
Fadhlaoui-Zid, K., Garcia-Bertrand, R., Alfonso-Sánchez, M. A., Zemni, R., Benammar-Elgaaied, A., & Herrera, R. J. (2014). Sousse: extreme genetic heterogeneity in North Africa. Journal of Human Genetics, 1-9. doi:10.1038/jhg.2014.99
Feldman, M., Master, D. M., Bianco, R. A., Burri, M., Stockhammer, P. W., Mittnik, A., . . . Krause, J. (2019). Ancient DNA sheds light on the genetic origins of early Iron Age Philistines. Science Advances, 5(7), 1-10. doi:10.1126/sciadv.aax0061
Greek DNA Project . (2019, July 21). Greek DNA Project – Y-DNA Classic Chart. Retrieved from Family Tree DNA: https://www.familytreedna.com/public/Greece?iframe=yresults
Grugni, V., Battaglia, V., Hooshiar Kashani, B., Parolo, S., Al-Zahery, N., & al., e. (2012, July 18). Ancient Migratory Events in the Middle East: New Clues from the Y-Chromosome Variation of Modern Iranians. PLOS ONE. doi:10.1371/journal.pone.0041252
Grugni, V., Raveane, A., Mattioli, F., Battaglia, V., Sala, C., Toniolo, D., . . . Semino, O. (2018). Reconstructing the genetic history of Italians: new insights from a male (Y-chromosome) perspective. Annals of human biology, 44-56. doi:10.1080/03014460.2017.1409801
Hay, M. (2018, September 28). Haplogroup J2. Retrieved from Eupedia: https://www.eupedia.com/europe/Haplogroup_J2_Y-DNA.shtml
Heraclides, A., Bashiardes, E., Fernández-Domínguez, E., Bertoncini, S., Chimonas, M., & Christofi, V. (2017). Y-chromosomal analysis of Greek Cypriots reveals a primarily common pre-Ottoman paternal ancestry with Turkish Cypriots. PLOS ONE, 12(6). doi:doi.org/10.1371/journal.pone.0179474
Herrera, K. J., Lowery, R. K., Hadden, L., Calderon, S., Yepiskoposyan, L., Regueiro, M., . . . Herrera, R. J. (2012). Neolithic patrilineal signals indicate that the Armenian plateau was repopulated by agriculturalists. European Journal Of Human Genetics, 20, 313-320. doi:10.1038/ejhg.2011.192
Hou, Y. (2019). Y-SNP Branch Information on L. Retrieved from YHRD: https://yhrd.org/tools/branch/L
Hungarian_Magyar_Y-DNA_Project. (2019, July 29). Family Tree DNA – Hungarian_Magyar_Y-DNA_Project. Retrieved from Family Tree DNA: https://www.familytreedna.com/public/Hungarian_Magyar_Y-DNA_Project?iframe=yresults
Immel, U. D. (2008, July 3). Population Tripoli, Libya [Libyan]. Retrieved from YHRD: https://yhrd.org/YP000416-Tripoli%2C+Libya+%5BLibyan%5D
ISOGG. (2019, July 31). Y-DNA Haplogroup Tree. Retrieved from ISOGG (International Society of Genetic Genealogy): https://isogg.org/tree/
Jankova, R., Geppert, M., Videtic Paska, A., Willuweit, S., & Roewer, L. (2019). Y-chromosome diversity of the three major ethno-linguistic groups in the Republic of North Macedonia. Forensic Science International: Genetics. doi:doi.org/10.1016/j.fsigen.2019.07.007
Karachanak, S., Grugni, V., Fornarino, S., Nesheva, D., Al-Zahery, N., Battaglia, V., . . . Semino, O. (2013). Y-Chromosome Diversity in Modern Bulgarians: New Clues about Their Ancestry. PLoS ONE, 8(3), 1-9. doi:10.1371/journal.pone.0056779
Karafet, T. M., Bulayeva, K. B., Nichols, J., Bulayev, O. A., Gurgenova, F., Omarova, J., . . . Hammer, M. F. (2016). Coevolution of genes and languages and high levels of population structure among the highland populations of Daghestan. Journal of Human Genetics, 181–191. doi:10.1038/jhg.2015.132
Karafet, T. M., Mendez, F. L., Meilerman, M. B., Underhill, P. A., Zegura, S. L., & Hammer, M. F. (2008). New binary polymorphisms reshape and increase resolution of the human Y chromosomal haplogroup tree. Genome research, 18(5), 830-838. doi:10.1101/gr.7172008
Karafet, T., Mendez, F., Meilerman, M., Underhill, P., Zegura, S., & Hammer, M. (2008). New binary polymorphisms reshape and increase resolution of the human Y chromosomal haplogroup tree. Genome Research, 830-839. doi:10.1101/gr.7172008
Kim, S. H., Han, M. S., Kim, W., & Kim, W. (2010, November). Y chromosome homogeneity in the Korean population. International Journal of Legal Medicine, 124(6), 653–657. doi:doi.org/10.1007/s00414-010-0501-1
Klyosov, A. A., & Kilin, V. V. (2016). Kilin-Klyosov TMRCA Calculator for Time Spans up to Millions of Years. Advances in Anthropology, 6(3), 51-71. doi:http://dx.doi.org/10.4236/aa.2016.63007
Kohl, P. L. (2007). The Making of Bronze Age Eurasia. New York: Cambridge University Press.
Lazaridis, I., Nadel, D., Rollefson, G., Merrett, D. C., Rohland, N., Mallick, S., . . . Reich, D. (2016). Genomic insights into the origin of farming in the ancient Near East. Nature, 2016/07/25/online. doi:10.1038/nature19310
Macedonian DNA. (2019, July 23). Macedonian DNA. Retrieved from Family Tree DNA: https://www.familytreedna.com/groups/macedonia/about/background
Mahal, D. G., & Matsoukas, I. G. (2017). Y-STR Haplogroup Diversity in the Jat Population Reveals Several Different Ancient Origins. Frontiers in Genetics, 8:121. doi:10.3389/fgene.2017.00121
Margaryan, A., Lawson, D., Sikora, M., Racimo, F., Rasmussen, S., Moltke, I., . . . de Barros Damgaard, P. (2019). Population genomics of the Viking world. bioRxiv. doi:10.1101/703405
Mršić, G., Petek, M., Vrdoljak, A., Popović, M., Valpotić, I., Anđelinović, Š., . . . Primorac, D. (2012). Croatian national reference Y-STR haplotype database. Molecular Biology Reports, 39, 7727–7741. doi: 10.1007/s11033-012-1610-3
Narasimhan, V. M., Patterson, N., Moorjani, P., Lazaridis, I., Lipson, M., Mallick, S., . . . Coppa, A. (2018). The Genomic Formation of South and Central Asia. bioRxiv. doi:10.1101/292581
Noveski, P., Trivodalieva, S., Efremov, G., & D., P.-K. (2010). Y chromosome single nucleotide polymorphisms typing by SNaPshot MINISEQUENCING. Balkan Journal of Medical Genetics, 13(1), 1-13. doi:10.2478/v10034-010-0013-9
Rosser, Z., Zerjal, T., Hurles, M., Adojaan, M., Alavantic, D., & Amorim, A. (2000). Y-Chromosomal Diversity in Europe Is Clinal and Influenced Primarily by Geography, Rather than by Language. Am J Hum Genet, 67(6), 1526-43.
Sahoo, S., Singh, A., Himabindu, G., Banerjee, J., Sitalaximi, T., Gaikwad, S., . . . Kashyap, V. K. (2006, January 24). A prehistory of Indian Y chromosomes: Evaluating demic diffusion scenarios. PNAS, 103(4), 843–848. doi:10.1073/pnas.0507714103
Scozzari, R., Cruciani, F., Pangrazio, A., Santolamazza, P., Vona, G., & Moral, P. (2001). Human Y-chromosome variation in the western mediterranean area: Implications for the peopling of the region. Human Immunology, 871-884. doi:doi.org/10.1016/S0198-8859(01)00286-5
Semino, O., Passarino, G., Oefner, P. J., Lin, A. A., Arbuzova, S., Beckman, L. E., . . . Francalacci, P. (2000). The Genetic Legacy of Paleolithic Homo sapiens sapiens in Extant Europeans: A Y Chromosome Perspective. Science, 290(5494), 1155-1159. doi:10.1126/science.290.5494.1155
Sengupta, S., Zhivotovsky, L. A., King, R., Mehdi, S. Q., Edmonds, C. A., Chow, C. E., & Underhill, P. A. (2006). Polarity and Temporality of High-Resolution Y-Chromosome Distributions in India Identify Both Indigenous and Exogenous Expansions and Reveal Minor Genetic Influence of Central Asian Pastoralists. The American Journal of Human Genetics, 78, 202–221. doi:10.1086/499411
The Y Chromosome Consortium. (2002). A Nomenclature System for the Tree of Human Y-Chromosomal Binary Haplogroups. Genome Research, 12(2), 339–348. doi:10.1101/gr.217602
Trivedi, R., Sahoo, S., Singh, A., Bindu, G. H., & Banerjee, J. (2007). High Resolution Phylogeographic Map of Y-Chromosomes Reveal the Genetic Signatures of Pleistocene Origin of Indian Populations. Anthropology Today: Trends, Scope and Applications, 393-414.
Völgyi, A., Zalán, A., Szvetnik, E., Nagy, M., & Pamzsav, H. (2014, October 31). Population Uzbekistan. Retrieved from YHRD: yhrd.org
Wang, C.-C., Reinhold, S. R., Kalmykov, A., Wissgott, A., Brandt, G., & al., e. (2018, May 16). The genetic prehistory of the Greater Caucasus. BioRxiv. doi:10.1101/322347
Wang, C.-C., Wang, L.-X., Zhang, M., Yao, D., Jin, L., & Li, H. (2013). Present Y chromosomes support the Persian ancestry of Sayyid Ajjal Shams al-Din Omar and Eminent Navigator Zheng He. arXiv, 1-5. Retrieved from https://arxiv.org/ftp/arxiv/papers/1310/1310.5466.pdf
Y Haplogroup L Project. (2019, June). L – Y Haplogroup L. Retrieved from Family Tree DNA: https://www.familytreedna.com/groups/y-haplogroup-l/about
YFull. (2019, April 2). YFull YTree v7.02.01. Retrieved from YFull: https://www.yfull.com/tree/L/
Zalloua, P. A., Xue, Y., Khalife, J., Makhoul, N., Debiane, L., & Platt, D. E. (2008). Y-Chromosomal Diversity in Lebanon Is Structured by Recent Historical Events. Am J Hum Genet, 873–882. doi:10.1016/j.ajhg.2008.01.020
[1] Најближи заједнички предак, у даљем тексту и скраћено као НЗП.
[2] Посматрајући Европу у геграфском смислу.
[3] Укупно је анализирано 442 скелета, од чега је 300 мушких.
[4] 847 ± 65 нове ере.
[5] Етнички састав Авганистана и унутар етнички односи L-M20 хаплогрупе су следећи: 42.1% Паштуни, 7,5%→518.516; 33.6% Таџици, 6,33%→349.271; 10.6% Узбеци, 9,44%→164.322; 9.8% Хазари, 3,9%→ 62.764; 3.9% Остали →Непознато.
[6] Према резултату Дибирове на 933 узорка евроазијске степе, а која укључује и Монголију, заступљеност L-M20 хаплогрупе је 0,5%.
[7] Према резултатима Таџика из Авганистана, заступљеност L-M20 хаплогрупе је 6,33%.
[8] Један од 3 резултата из којих је извучен Y хромозом.
[9] Филестејци су по писању народ за који се сугерише културна веза с микенским свијетом у Грчкој и индоевропски језик.


































25. август 2019. у 20:52
Defendor
Браво на сјајном чланку! 🙂
13. новембар 2019. у 22:23
Данило
Одличан текст и велики труд за хаплогрупа која је у ,,минималном” проценту заступљена код Срба.
Међутим из свега написаног шта је основа ,,ЛТ” хаплогрупе која РАСА или подраса?…Шта би био изворни и најдоминантнији фенотип једног ,,Л” човека?
19. новембар 2019. у 21:50
E.K.
According to Maciamo, founder of Eupedia; L1b1 (M349) has been found in Italy, Switzerland, Austria, Germany, Belgium, England, northern Ireland, and scattered around most of central and eastern Europe and the eastern Mediterranean. The presence of L1b and L1b1 in Europe probably dates back to the Neolithic period.
There’s also Scandinavian samples of L-M349 from Norway and Sweden on yFull.
Th fact that this haplogroup is so minor yet vastly spread in Europe tells us simply nothing. According to yFull, L-M349 was formed 12400 years ago and the fact that it concentrates mostly in Europe strenghtens Maciamo’s suggestions about L-M349’s european Neolithic ancestry. It’s ancestor clade, L-M317 is heavily concentrated in Caucasus and it’s age is according to yFull 18200 years.
By far, a lot of the L-M349 inviduals have ancestry from mountainous areas of Europe.
A reply to your question; L-M349’s original phenotypes would be the same as other haplogroups’ during the Neolithic period.
16. децембар 2022. у 01:27
Petar
Ima li medju Srbima pripadnika podgrana L-M357 i L-M27 ?
30. април 2023. у 19:27
Miloš
U Hercegovini ima familija koje pripadaju grani L-M357, (“Hercegovački Poduhvat”)